readxl |> library()
dplyr |> library()
tidyplots |> library()
ggtext |> library()
hifi <- "raw_data/2026-03-27_proofread-dna-polymerases.xlsx" |>
readxl::read_xlsx(col_names = TRUE)
hifi <- hifi |>
mutate(dna_polymerase_provider = paste(`proofread-dna-polymerase`, provider_1, sep = "_"))
hifi <- hifi |>
mutate(domestic = as.factor(domestic))
hifi |> tidyplots::tidyplot(x = dna_polymerase_provider, y = `fidelity-than-taq`, color = domestic) |>
add_sum_bar(alpha = 0.2) |>
add_sum_dash() |>
add_sum_value(accuracy = 1, color = "black") |>
sort_x_axis_levels() |>
adjust_x_axis(rotate_labels = TRUE, title = "") |>
adjust_y_axis_title("Fidelity, relative to *Taq*") |>
adjust_size(width = 100) |>
adjust_legend_title("Domestic?") |>
adjust_legend_position(position = "top") |>
adjust_font(family = "mono") |>
adjust_title("High-fidelity DNA polymerases", face = "bold") |>
adjust_caption(paste("Fidelity/保真性数据来自其官网。", "国内公司用中文对应的首字母缩写表示。", "没有尝试统计所有可能的公司。", sep = "\n")) |>
add(ggplot2::theme(axis.title.y = ggtext::element_markdown())) |>
save_plot("images/2026-03-29_high-fidelity-dna-polymerases.png")3 High-fidelity DNA polymerases
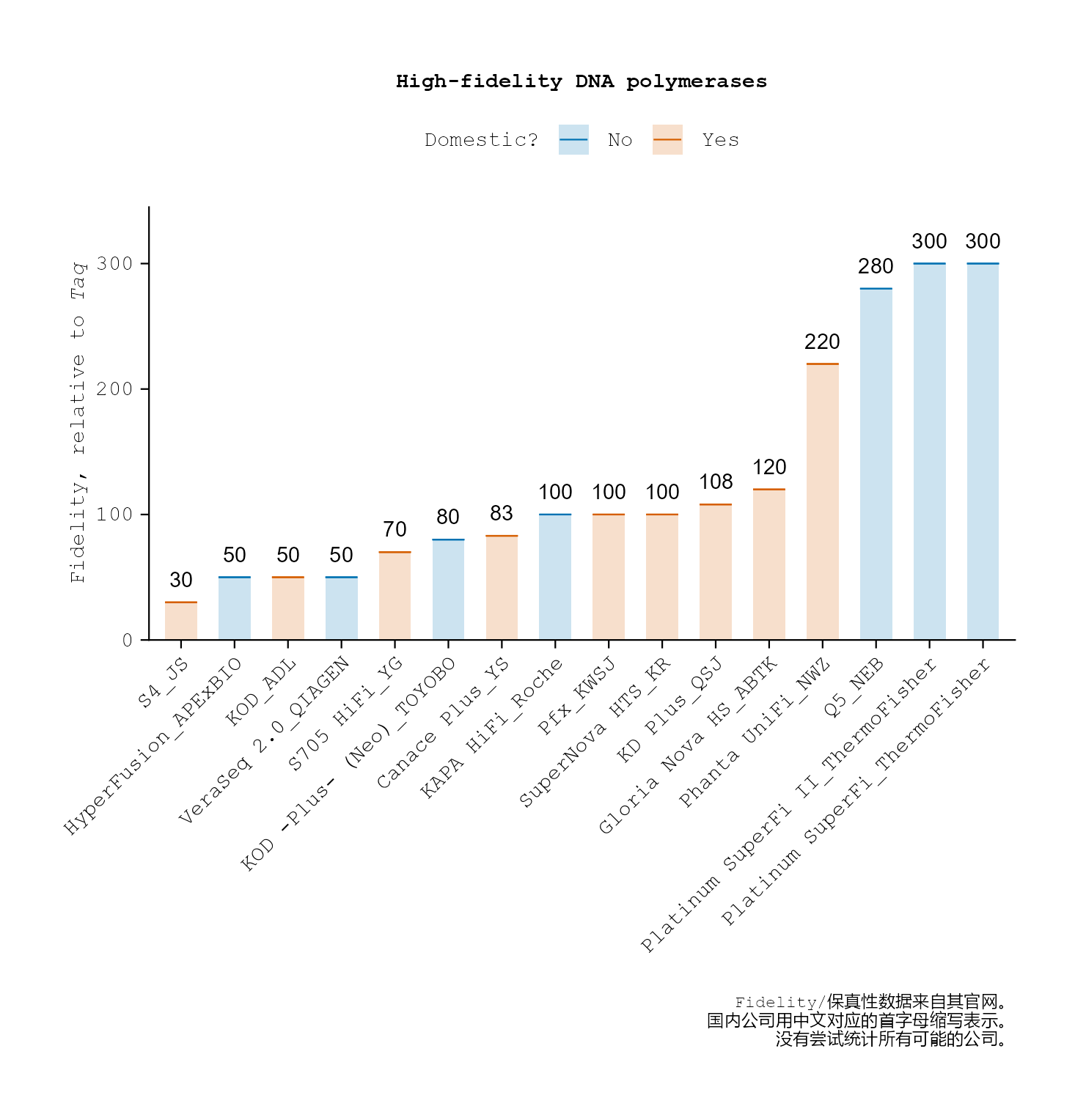
The high-fidelity capacity of DNA polymerases compared to Taq DNA polymerase
几乎每个和生物相关的个人可能都用过高保真DNA聚合酶(high-fidelity DNA polymerase)。
这里较系统的比较不同公司的高保真DNA聚合酶的保真性(相比于Taq DNA聚合酶)。
Note
一个公司大概选一种保真性最高的DNA聚合酶(若该公司有多种高保真DNA聚合酶)。
保真性参数来自其公司产品网页的描述(因此数据真实性由公司负责)。
若某个公司未提及其高保真DNA聚合酶的保真性参数(即相比于Taq DNA聚合酶),则不统计该酶。
1. 读取整理的数据表格并展示
以下是R code。
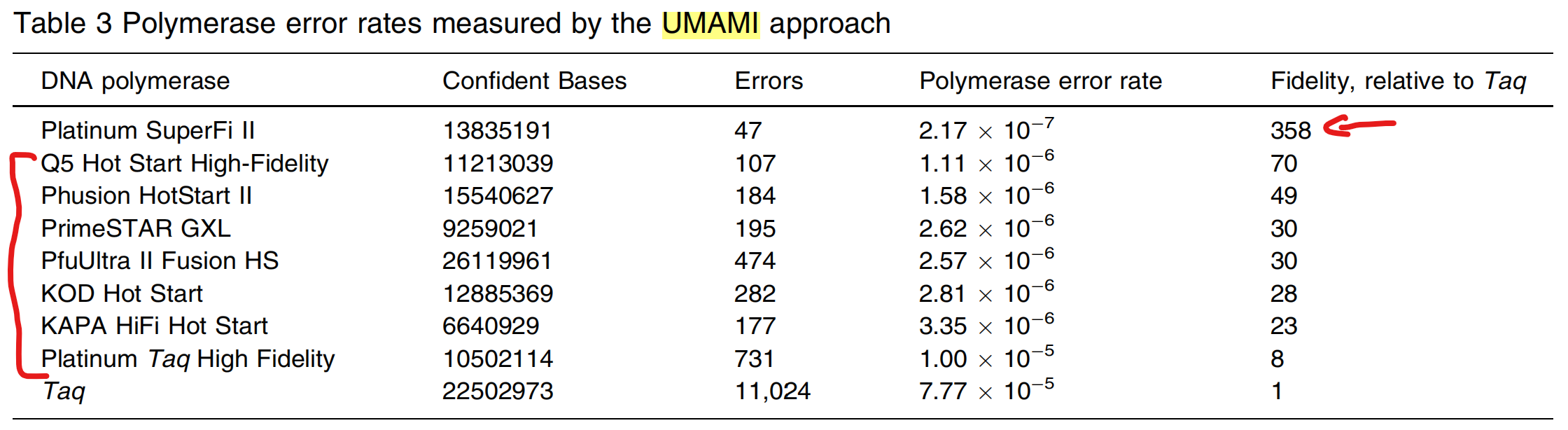
2. ThermoFisher公布的测试比较
ThermoFisher于2021年(1)基于Unique MuA-based Molecular Indexing(UMAMI)技术策略比较了几种高保真DNA聚合酶的保真性。
References
1.
P. Mielinis, R. Sukackaitė, A. Serapinaitė, F. Samoilovas, G. Alzbutas, K. Matjošaitis, A. Lubys, MuA-based molecular indexing for rare mutation detection by next-generation sequencing. Journal of Molecular Biology 433, 167209 (2021).